Sota el nom de “DNA barcoding” s’entén la identificació d’un grup d’organismes mitjançant un fragment curt d’ADN. Quan l’ADN utilitzat procedeix de mostres ambientals (d’ADN ambiental o eDNA), hom parla de “eDNA barcoding”. I quan es tracta d’utilitzar aquest ADN ambiental per identificar comunitats senceres, es parla de “eDNA metabarcoding”. Eva Garcia-Vazquez i Alba Ardura, del Departament de Biologia Funcional de la Universitat d’Uviéu, treballen en l’aplicació de l’eDNA metabarcoding en l’estudi de la comunitat zooplanctònica pel que fa a larves de peixos i els llurs depredadors. Les larves dels primers estadis, de difícil identificació visual, són la “biomassa perduda”, i trobar-la ajudaria en la gestió de pesqueries. Garcia-Vazquez i Ardura, juntament amb Oriane Georges i Sara Fernandez, publiquen a la revista Scientific Reports un article sobre l’aplicació d’aquesta tècnica en la detecció d’espècies zooplanctòniques d’interès per a pesqueries d’aigües litorals i obertes. Garcia-Vazquez et al. treballen a partir de mostres ambientals d’aigua d’uns 6 litres cadascuna, procedents de diferents punts de l’Oceà Atlàntic, la Mar Mediterrània, la Mar Roja i l’Oceà Pacífic. Hi apliquen una seqüenciació massiva del gen citocrom-oxidasa I (COI), que és el que fa de “codi de barres”: és un gen que participa en la respiració mitocondrial, activitat metabòlica comuna a un ample ventall d’organismes, relativament conservat, i que des de fa dècades s’utilitza com a rellotge molecular en estudis evolutius. El “metabarcode” posa de manifest les espècies més abundants de cada mostra, i Garcia-Vazquez et al. detecten diverses espècies de peixos i d’invertebrats de rellevància pesquera (els primers com a captura, els segons com a aliment dels primers), i confirmen aquestes deteccions mitjançant una ulterior lectura individual. És interessant que trobin una menor profunditat taxonòmica en les mostres d’aigües tropicals en comparació amb les temperades, cosa que atribueixen al fet que les bases de dades de referències tinguin un biaix cap a les espècies temperades. Per això recomanen enfortir la introducció de seqüències del gen COI i d’altres “codis de barres” pel que fa a les espècies tropicals. El més rellevant és que la tècnica ofereix la possibilitat de fer una detecció més o menys quantitativa de la presència de larves de peixos d’interès pesquer ja en els primers estadis de desenvolupament, així com de les seves preses i dels seus depredadors.
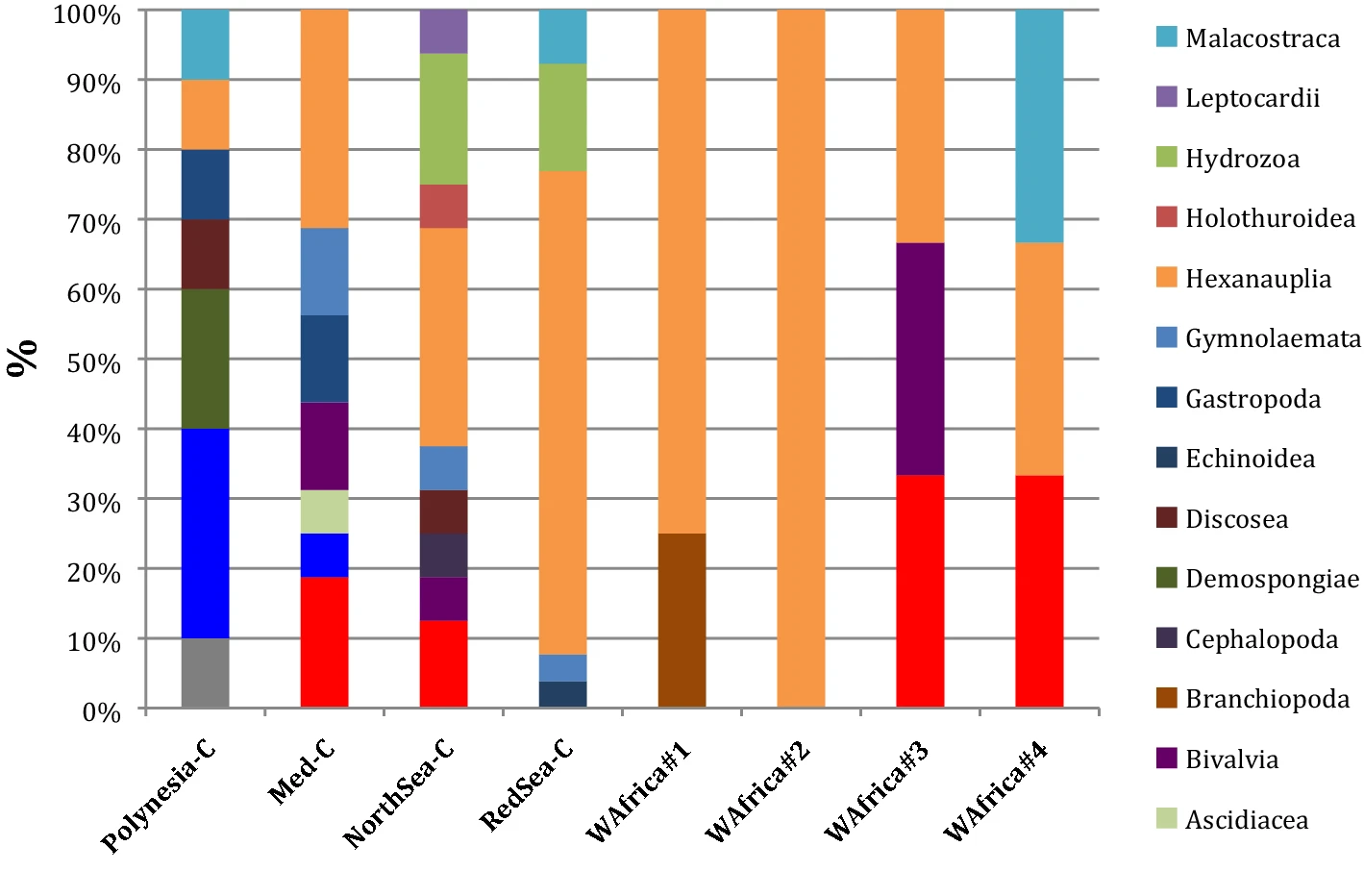
Diversitat taxonòmica del zooplàncton d’aigües de diferents mars del planeta
La lectura simultània de codis de barres genètics en mostres de zooplàncton
Aquesta recerca fou concebuda i dissenyada per Eva García-Vázquez i Alba Ardura. García Vázquez és catedràtica de genètica de la Universidá d’Uviéu. Alba Ardura Gutiérrez té un contracte Juan de la Cierva en l’Àrea de Genètica del Departamento de Biología Funcional de la mateixa universitat. En el mostreig participà, a més de García-Vázquez i d’Ardura, Oriane Georges, del mateix departament universitari, i agraeixen a la tripulació del Polarstern l’assistència en la recol·lecció de les mostres atlàntiques durant els creuers de recerca PS102 i PS116, especialment a Anastasija Zaiko, Serge Planes, Martin Desmalades i Johannes Rick. La feina al Polastern fou finançada pel projecte AWI_PS116_00 de l’Institut Alfred Wegener. En l’anàlisi de laboratori, a més d’Ardura i Georges, participà Sara Fernandez, investigadora post-doctoral al Department of Natural Sciences de l’Institiúd Teicneolaíochta na Gaillime-Maigh Eo. L’anàlisi de la seqüenciació fou duta a terme per Ardura, Fernández i Georges. García-Vázquez realitzà l’anàlisi estatística. La recerca fou finançada amb els projectes IDI-2018-000201 del Govern del Principat d’Astúries, i el GLOBALHAKE PID2019-108347RB-I00 del Ministeri de Ciència i Innovació del Regne d’Espanya. Ardura i García-Vázquez redactaren l’article, que fou revisat per les altres autores, les quals agraeixen la correcció realitzada per Aida Dopico. Ardura, com a autora corresponsal, trameté l’article a Scientific Reports el 30 de desembre del 2020, que l’acceptà el 19 de març i el publicà el dia 31.
Moltes espècies de peixos d’interès comercial tenen una fase larvària més o menys perllongada en la que integren el zooplàncton, és a dir el conjunt d’animals que suren (en contraposició als que neden, el zoonècton, del qual formaran part en la fase ulterior del seu cicle vital). Aquesta fase larvària planctònica és sovint encara desconeguda o poc estudiada per a moltes espècies, i per això les autores parlen de “biomassa perduda”. D’especial rellevància són les xarxes tròfiques del zooplàncton, tant perquè en ell hi troben preses (com els copèpodes per a les larves del lluç), com perquè les larves dels primers estadis són aliment per les larves de la mateixa espècie d’estadis ulteriors. Tant el zooplàncton en general, com l’ictioplàncton en particular, mostren signes d’afectació pel canvi global: la pujada de les temperatures oceàniques pot constituir una amenaça addicional per a la sostenibilitat de pesqueries en aigües temperades i tropicals.
Tradicionalment, les comunitats planctòniques s’estudiaven a través de la filtració de grans volums d’aigua recollida en campanyes oceanogràfiques. La filtració permet la concentració del plàncton de cada a fer una identificació visual d’individus, bé a la lupa o al microscopi. Sovint, es fa difícil fer una identificació visual d’una larva de peix, car moltes espècies són críptiques (s’assemblen massa les unes a les altres).
Des de fa uns anys, el grup de Garcia-Vazquez treballa amb l’aplicació del “DNA barcoding” en estudis ictioplanctònics. D’entrada aquesta lectura de seqüències concretes d’ADN s’aplica a la identificació d’espècimens individuals, però amb el desenvolupament de la seqüenciació massiva es possible aplicar-la també directament a mostres d’aigua. S’hi fa una extracció total de l’ADN d’aquesta mostra ambiental (ADN ambiental o eDNA), i s’hi obtenen milions de seqüències del gen que faci de codi de barres. L’avantatge d’aquesta aproximació és el seu caràcter no-destructiu, car hom analitza l’ADN present en el medi, és a dir l’ADN que ha estat alliberat pels organismes.
La qualitat de les dades obtingudes depèn de totes i cadascuna de les passes implicades: 1) el mostreig; 2) l’extracció d’ADN; 3) el disseny dels encebadors de la reacció en cadena de la polimerasa (PCR); 4) la tècnica de seqüenciació; 5) l’anàlisi bioinformàtica de les seqüències obtingudes.
El gen de la citocrom oxidasa I (COI) té algunes seqüències molt ben conservades entre tots els metazous, la qual cosa ajuda a fer-lo servir com a codi de barres per a comunitat zooplanctòniques. El gen de l’ARN ribosomal 18S s’utilitza per a estudis de tot el plàncton, ja que abasta una diversitat biològica encara més àmplia (tots els eucariotes), però la seva resolució filogenètica, en conseqüència, és menor.
El metabarcoding pot ser una tècnica ben sensible: en mostres de 3 L ja és possible detectar espècies molt minoritàries. La concentració zooplanctònica varia força entre les aigües litorals (amb fins a 50.000 individus per metre cúbic) i alta mar (menys de 500 individus per metre cúbic). A la Mediterrània en aigües obertes, hi ha oscil·lacions considerables en la biomassa planctònica, pasant de 0,8 mg·m-3 a 34,5 mg·m-3.
Garcia-Vazquez et al. seleccionaren les mostres emprades en aquest estudi a través de dues contraposicions: a) aigües obertes i aigües costaneres; b) aigües subtropicals i aigües tropicals. Així doncs, l’Oceà Atlàntic és representat per aigües obertes subtropicals (WA #1), aigües obertes tropicals (WA #2, WA #3 i WA #4), aigües davant del port de Bremerhaven (octubre del 2016), l’Estany de Provost (a l’Erau, el desembre del 2016), al Golf d’Aqaba (a la Mar Roja, entre les platges de Red Rock i Neviot, el gener del 2019) i a l’atol de Rangiroa (a la Polinèsia, el febrer del 2018).
De cadascun d’aquests punts s’analitzaren mostres de 6 L. Les mostres d’aigües obertes foren obtingudes el novembre del 2018 en el PS116 del RV Polarstern. Aquestes mostres eren concentrades a través de filtres amb una mida de por de 0,2 μm. Els concentrats eren codificats i conservats en etanol absolut. Paral·lelament es feia un estudi clàssic a partir de mostres recollides amb una xarxa de malla de 20 μm (uns 200 litres concentrats en tres replicats de 50 mL): els individus zooplanctònics eren observats sota el microscopi i identificats amb l’ajut de guies, i alguns espècimens eren conservats en etanol per a un DNA barcoding, i d’altres en formaldehid al 10%.
La mostra mediterrània consistí en 6 litres d’aigua superficial de l’Estanh Provost, recollides en tres ampolles estèrils de 2 L, passades per filtres de polieterfulsona d’una mida de por de 0,2 μm.
La mostra polinèsia consistí en 6 litres d’aigua recollides en dues ampolles, i filtrats immediatament amb una mida de por de 0,2 μm.
La mostra del Golf d’Aqaba es prengué del litoral amb un sistema de filtració de 0,2 μm.
La mostra de la Mar del Nord es collí al port de Bremerhaven: 6 L de 3 mostres de 2L cadascuna, que foren filtrades en membranes amb una mida de por de 0,2 μm.
En tots aquests casos els filtres eren conservats en etanol a temperatura ambient fins a l’extracció d’ADN ambiental. El material de mostreig (guants, xeringa, poal, etc.) era estèril, i abans i després de cada operació se’l rentava amb una solució al 5% d’hipoclorit sòdic, i seguidament s’esbandia tres vegades amb aigua estèril neta.
En el creuer PS102 de novembre del 2016 es collien mostres més petites, amb un cubell de 1,5 L, que també eren filtrades en membranes de malla de 0,2 μm. Aquestes mostres representaven latituds entre 48,49 N fins a 22,22 S des de la Mar del Nord a l’Atlàntic Sud.
L’extracció d’ADN dels filtres es feia amb el PowerWater DNA Isolation Kit de Qiagen. Per a les mostres de Polarstern s’empraven els encebadors universals del gen COI mlCOIintF i jgHCO2198, modificats amb un adaptador per distingir les lectures de cada mostra. Tant en l’extracció com en la PCR s’incloïen controls negatius. Els amplicons obtinguts eren visualitzats en un gel d’agarosa del 2%, del qual es recuperaven amb el Montage DNA Gel Extraction Kit de Millipore.
Per a les altres mostres, s’utilitzaven els mateixos encebadors, però amb adaptadors per fer l’amplificació en la plataforma Illumina. La genoteca resultant era seqüenciada en aquesta mateixa plataforma.
Per al barcoding individual s’extreia ADN dels espècimens congelats. En aquest cas es feia una amplificació semblant del gen COI i també un altre d’un fragment de 400-600 parells de nucleòtids del gen 18S rRNA (amb els primers Uni18SF i Uni18SR). La purificació i seqüenciació es feia en la Unitat de Seqüenciació de la Universitat d’Oviedo. Les seqüències obtingudes eren analitzades per BLAST respecte la base de dades GenBank. La informació taxonòmica era comprovada en el Registre Mundial d’Espècies Marines.
L’anàlisi bioinformàtica de les dades de seqüenciació arrencava amb l’eliminació dels adaptadors i dels encebadors. Es retenien els amplicons de 200 a 400 parells de nucleòtids. Les seqüències filtrades eren comparades amb la base de dades de NCBI del gen COI (“COI NOT Bacteria NOT environmental NOT viruses NOT unclassified”). Per a l’assignació taxonòmica s’exigia un percentatge d’identitat del 97%.
D’aquest processament deriven taules d’unitats taxonòmiques operatives (OTUs). Amb una inspecció manual s’eliminaven de les taules OTUs les espècies no-marines. Les anàlisis següents només es feien sobre espècies que, d’acord amb el llur cicle biològic, fossin teòricament presents en el plàncton de l’àrea mostrejada en l’època de mostreig. Tan sols les espècies zooplanctònics foren considerades. Per estimar la diversitat utilitzaren l’índex D de Brillouin, que té en compte, a diferència de l’índex de Shannon, la diferència entre la “taxa de captura” de cada espècie. Les diferències entre mostres eren visualitzades amb una escala no-mètrica tridimensional (NMDS), d’acord amb la presència o absència de l’ADN de cada espècie.
Les mostres temperades/subtropicals foren comparades amb les tropical amb un test de Mann-Whitney pel que fa a la precisió taxonòmica de l’assignació (és a dir, segons el percentatge d’OTUs assignades a una espècie).
Les mostres de l’expedició PS 102 del Polarstern
De les mostres de 1,5 L recollides en el creuer PS 102, tan sols la presa prop de la costa, a l’inici del viatge, amb 457 lectures, donà seqüències taxonòmicament assignades a invertebrats marins: quatre poliquets (Gyptis propinqua, Lumbrineris latreilli, Paradoneis ilvana, Polycirrus sp.) i un malacostraci (Pisidia longicornis). En les altres set mostres d’ADN ambiental no s’hi detectaren animals marins, però sí algunes lectures d’Homo sapiens i d’insectes, atribuïbles a una contaminació. Volums tan petits no semblen adients per a una tècnica de metabarcode per a zooplàncton.
Els resultats de les mostres ambientals de 6 L
En les mostres de 6 L, el nombre de lectures de qualitat no diferia entre els llocs de mostreig. El nombre d’OTUs zooplanctòniques detectades anava de 5.343 (WA, West Africa #1) a 22.649 (WA #4). Dins d’aquest rang hom trobava les mostres litorals, des dels 6.294 de Rangiroa a 14.794 de l’Estanh Provost.
Sí que variava la proporció de seqüències assignades a espècies animals planctòniques, i que la proporció sobre el total d’OTUs oscil·lava entre el 10% (WA #2) i el 40%. Les OTUs no-zooplanctòniques eren bé de grans animals (a mar obert davant de l’Àfrica Occidental) o de fitoplàncton (en les mostres costaneres). La detecció de l’ADN de grans animals (cetacis i taurons) s’explica perquè, a major mida corporal, hi ha un major despreniment d’ADN que passa a l’ambient.
Les mostres d’aigües temperades i subtropicals (Bremerhaven, Aqaba, Provost, Illes Canàries) eren les que tenien una major profunditat d’assignació taxonòmica, amb més de 60% d’OTUs corresponents a espècies. En tres de les mostres tropicals, més de la meitat de les OTUs es corresponien a categories taxonòmiques superiors (gènere, família o ordre). Aquesta diferència entre mostres extratropicals i tropicals era significativa.
El zooplàncton d’aigües obertes de l’Àfrica Occidental
En les mostres d’aigües obertes de l’Àfrica Occidental s’identificaren per metabarcode tres espècies de copèpodes (Clausocalanus furcatus, Delibus nudus, Paracalanus nanus), una de cladòcer (Evadne cf. spinifera), una d’eufàsid (el krill Euphausia sp.), una de bivalve (Magallana gigas) i una de peix (Engraulis encrasicolus). Ja fora del zooplàncton s’identificaven altres vertebrats i OTUs de fitoplàncton. El nombre d’espècies de zooplàncton detectades en cada localitat era baixa: 1 a WA #2, 3 a WA #3 i a WA #4 i 4 a WA #1.
Les espècies trobades per metabarcode es podien confirmar amb la identificació visual tradicional. D’altres espècies, com l’apendiculari Oikopleura sp., l’equinoderm Styracaster paucispinus (en estadi larvari) i el poliquet Vanadis formosa s’identificaven per barcode individual, però no en el metabarcode. Recordem que en el metabarcode s’analitzaven mostres de 6 L, i en l’anàlisi visual mostres de 200 L.
De les espècies identificades en oceà obert per metabarcode, n’hi havia cinc d’especial importància per als recursos pesqueres: Paracalanus nanus i Euphasia, que són aliment de juvenils de lluç; Evadne spinifera i Clausocalanus furcatus, que són aliment de diversos peixos; i Engraulis encrasicolus, el seitó atlàntic, que no tan sols és rellevant en ell mateix (anxova) sinó també com a presa de de tonyines i d’altres espècies d’importància comercial per a les pesqueries africanes.

Seitons juvenils
El zooplàncton d’aigües litorals
El nombre d’espècies de zooplàncton detectades en aigües litorals per metabarcode és superior al d’aigües obertes, tot i que el nombre de lectures és semblant. Al Golf d’Aqaba es detecten 26 OTUs, al port de Bremerhaven 16, a l’Estanh Provost 16, i a Rangiroa 10. Pertanyen a diferents divisions del Regne Animal (6 phyla diferents a Bremerhaven i Rangiroa, 5 a Provost, i 4 a Aqaba. Diverses espècies detectades per metabarcode foren confirmades en barcodes individuals (com Mytilus galloprovincialis, Paracalanus parvus, Undinula vulgaris, Acartia clausii).

‘Paracalanus parvus’ és dels copèpodes l’ADN del qual es detectat en mostres d’aigües litorals
De les espècies zooplanctòniques (en l’estadi d’ou i de primera larva) més rellevants des del punt de vista pesquer que es detecten per metabarcode, Garcia-Vazquez et al. esmenten:
– Merlangius merlangus i Merluccius merluccius a la Mar del Nord.
– Chelon labrosus i Dicentrarchus labrax a la Mediterrània.
– els copèpodes Clausocalanus i Paracalanus, rellevants en l’alimentació de peixos d’interès pesquer.

La llissa vera (‘Chelon labrosus’) fotografia d’adult a Menorca. L’ADN d’aquesta espècie és detectable per metabarcode en mostres d’aigua recollida a la vora de l’Estanh Provost, al Lengadoc
L’aplicació del metabarcoding d’ADN ambiental en la gestió de pesqueries
Especialment per a les mostres litorals, n’hi hauria prou, doncs, amb 6 litres de mostra, per detectar per amplificació del gen COI els components més rellevants del zooplàncton, entre ells les larves de peixos d’interès pesquer i les llurs preses. Per a l’ictioplàncton, suposa un estalvi en quantitat de mostra necessària, i per al procés d’identificació individual (visual o per barcode individual) de cada ou i de cada larva.
L’aplicació d’aquesta tècnica requereix de seqüències de referència exhaustives i ben validades. BOLD és una base de dades dedicada a la identificació d’espècies mitjançant l’ADN, però Garcia-Vazquez et al. consideren GenBank com la base de dades més completa en termes de marcadors i d’espècies. L’única forma d’omplir els buits en aquestes bases de dades és amb el treball d’especialistes pelàgics locals amb perícia taxonòmica.
Amb una tècnica o altra, la finalitat és millorar l’inventari de la comunitat ictioplanctònica, aprofundir en el coneixement de la cadena tròfica i d’altres aspectes funcionals de l’ecosistema, i entendre’n la variabilitat en el temps i l’espai. Alhora, el metabarcode d’ADN ambiental tindria una utilitat pràctica en el monitoratge de les poblacions de les espècies més abundants.
Lligams:
– eDNA metabarcoding of small plankton samples to detect fish larvae and their preys from Atlantic and Pacific waters. Eva Garcia-Vazquez, Oriane Georges, Sara Fernandez & Alba Ardura. Sci. Rep. 11: 7224 (2021).